1. 背景:ENSO と南方振動指数
エルニーニョとラニーニャは、海洋と大気が結びついた変動であり、まとめて ENSO(El Niño-Southern Oscillation)と呼ばれる。エルニーニョ時には赤道太平洋東部で暖水が広がり、大気循環も平年と異なる。
その大気側の変動を表す代表的な指標のひとつが 南方振動指数(SOI) である。SOI は、タヒチとダーウィンの海面気圧の変動を用いて計算される。
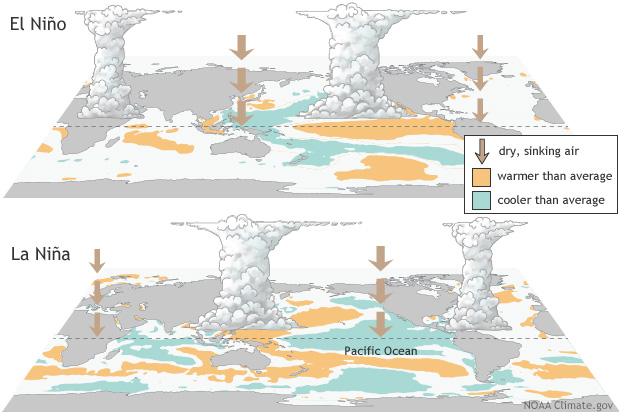
エルニーニョ時(上)は赤道太平洋東部で暖水が広がり、ラニーニャ時(下)は逆に冷水が強まる。これに対応して大気循環も変化する。
2. 使用データ
本演習では、タヒチおよびダーウィンの月平均海面気圧データを用いる。ファイルはこのページと同じディレクトリに置いてある。
2025年4月以降は -99.9 で欠損が入っている。Python ではこれを NaN として読ませる。
3. 計算の流れ
- タヒチ・ダーウィンの海面気圧データを読み込む
- 1981–2010 年を基準期間として climatology(各月平均)を求める
- anomaly(平均からのずれ)を計算する
- 標準偏差を用いて標準化する
- MSD(標準化した差のばらつき)を求める
- SOI を計算する
- 時系列として描画する
NOAA/CPC に従い、平均の基準期間は 1981–2010 とする。
4. Pythonでよく出る機能の意味
SOI の計算では、計算そのものより前に、データの形を整える操作がたくさん出てくる。ここを飛ばすと、コードを読んでいて急に難しく感じる。
| 書き方 | 意味 |
|---|---|
| pd.read_csv(...) | 表形式データを読む。今回は空白区切りテキストを表として読む。 |
| set_index("YEAR") | YEAR 列を行ラベルにする。年でデータを選びやすくなる。 |
| .loc[1981:2010, months] | 行と列をラベルで指定して切り出す。前は年、後ろは月名。 |
| mean(axis=0) | 列ごとに平均する。各月の平均を求めるときに使う。 |
| to_numpy() | pandas の表を NumPy 配列に変える。 |
| ravel() | 2次元配列を1次元に並べ直す。 |
| np.isnan(...) | 欠損値 NaN かどうかを調べる。 |
| enumerate(...) | 中身と番号を同時に取り出す。 |
| pd.DataFrame(...) | 辞書や配列から表を作る。 |
大事な見方
Python の長いコードは、「計算式」と「データの形を整える部分」に分けて読むとわかりやすい。
Python の長いコードは、「計算式」と「データの形を整える部分」に分けて読むとわかりやすい。
STEP 1
5. データの読み込み
まずは Python でテキストファイルを読み込む。ここでは pandas を用いる。
import numpy as np
import pandas as pd
import matplotlib.pyplot as plt
dar = pd.read_csv("Darwin.txt", sep=______, engine="python", na_values=[-99.9])
tah = pd.read_csv("Tahiti.txt", sep=______, engine="python", na_values=[-99.9])
print(dar.head())
print(tah.head())
print(dar.columns)
print(dar.shape)
print(dar.tail())ポイント
- sep は区切り文字の指定
- 今回は空白の数が一定でないので r"\s+" を使う
- na_values=[-99.9] により、欠損値を NaN として読む
- engine="python" は柔軟な読み込みを使う指定
このブロックで新しく出るもの
- pd.read_csv:表データを読む関数
- sep:何で区切られているかを指定する
- engine="python":少し柔軟な読み込み方法を使う指定
- na_values=[-99.9]:-99.9 を欠損値として扱う指定
- head():先頭数行を見る
- columns:列名一覧を見る
- shape:行数と列数を見る
- tail():末尾数行を見る
| sep | 意味 |
|---|---|
| "," | カンマ区切り |
| "\t" | タブ区切り |
| " " | スペース1個 |
| r"\s+" | 空白が1個以上 |
確認
- 列名はどのようになっているか
- 何年分のデータが入っているか
- 2025年4月以降の -99.9 はどのように読まれているか
STEP 2
6. climatology の計算
基準期間 1981–2010 年の各月平均を求める。これが climatology である。
months = ["JAN","FEB","MAR","APR","MAY","JUN",
"JUL","AUG","SEP","OCT","NOV","DEC"]
dar = dar.set_index("YEAR")
tah = tah.set_index("YEAR")
dar_base = dar.loc[______:______, months]
tah_base = tah.loc[______:______, months]
mslpd = dar_base.mean(axis=______)
mslpt = tah_base.mean(axis=______)
print(mslpd)
print(mslpt)
print(len(mslpd))
print(mslpd["JAN"], mslpd["AUG"])ポイント
- set_index("YEAR") により、年をインデックスとして使う
- .loc[行, 列] はラベルで範囲を指定して取り出す
- axis=0 は縦方向、つまり各月ごとの平均を意味する
確認
- mslpd には何個の値が入るか
- mslpd["JAN"] は何を意味するか
- axis=1 にすると何が起きるか
STEP 3
7. anomaly の計算
観測値から climatology を引いて anomaly(平均からのずれ)を求める。
aDar = dar[months] - ______
aTah = tah[months] - ______
print(aDar.head())
print(aTah.head())
print(aDar.loc[1981:2010].mean(axis=0))
print(aTah.loc[1981:2010].mean(axis=0))ポイント
- anomaly = 観測値 − climatology
- 単位はまだ hPa のまま
- 基準期間 1981–2010 の平均はおおむね 0 に近くなる
STEP 4
8. 標準化の計算
anomaly を標準偏差で割り、スケールをそろえる。
aDar_base = aDar.loc[1981:2010, months].to_numpy().ravel()
aTah_base = aTah.loc[1981:2010, months].to_numpy().ravel()
aDar_base = aDar_base[~np.isnan(aDar_base)]
aTah_base = aTah_base[~np.isnan(aTah_base)]
sDar = np.sqrt(np.sum(aDar_base**2) / ______)
sTah = np.sqrt(np.sum(aTah_base**2) / ______)
nDar = aDar / ______
nTah = aTah / ______
print(sDar, sTah)
print(nDar.head())
print(np.nanmean(nDar.loc[1981:2010, months].to_numpy()))
print(np.nanmean(nTah.loc[1981:2010, months].to_numpy()))ポイント
- to_numpy().ravel() により、30年×12ヶ月の表を 1 次元の配列にする
- 全データをまとめて 1 つの標準偏差を出したいので 1 列に並べる
- ~np.isnan(...) は NaN でない値だけを残す処理
- anomaly はすでに平均を引いた値なので、標準偏差は sqrt(sum(x^2)/N) で求められる
確認
- aDar.loc[1981:2010, months] の shape はどうなるか
- ravel() 後の shape はどうなるか
- 標準化後の値は単位を持つか
STEP 5
9. MSD の計算
標準化したタヒチとダーウィンの差のばらつきを MSD として求める。
diff_base = (nTah.loc[1981:2010, months]
- nDar.loc[1981:2010, months]).to_numpy().ravel()
diff_base = diff_base[~np.isnan(diff_base)]
MSD = np.sqrt(np.sum(diff_base**2) / diff_base.size)
print(MSD)ポイント
- MSD は 標準化した差 のばらつき
- SOI は単なる差ではなく、差をさらに標準化した指標である
STEP 6
10. SOI の計算
SOI = (______ - ______) / ______
print(SOI.head())SOI は、標準化したタヒチとダーウィンの差を MSD で割って求める。
確認
- 1951年1月の SOI の値はいくつか
- SOI の符号は NOAA の図と一致しているか
STEP 7
11. 描画とデータ保存
records = []
for year in SOI.index:
for imonth, month in enumerate(months, start=1):
records.append({
"YEAR": year,
"MONTH": imonth,
"SOI": SOI.loc[year, month]
})
soi_ts = pd.DataFrame(records)
soi_ts["TIME"] = soi_ts["YEAR"] + (soi_ts["MONTH"] - 1) / 12.0
soi_ts = soi_ts.dropna(subset=["SOI"])
plt.figure(figsize=(12,4))
plt.plot(soi_ts["TIME"], soi_ts["SOI"])
plt.axhline(0, color="k")
plt.xlabel("Year")
plt.ylabel("SOI")
plt.title("Southern Oscillation Index")
plt.show()
# 月別テーブル型
SOI_out = SOI.copy()
SOI_out.insert(0, "YEAR", SOI_out.index)
SOI_out.to_csv("SOI_monthly_table_updated.txt",
sep="\t", index=False, float_format="%.4f")
# 1次元時系列型
soi_ts.to_csv("SOI_timeseries_updated.txt",
sep="\t", index=False, float_format="%.4f")ポイント
- 2次元表の SOI を 1 次元の時系列に並べ直す
- 描画して、ENSO の時間変動を視覚的に確認する
- 計算した SOI を txt ファイルとして保存し、次回の課題で利用する
- to_csv(...) を使うと、表をテキストファイルとして保存できる
- sep="\t" はタブ区切りを意味する
- index=False は左端の行番号を保存しない指定である
確認
- 強い正・負の期間はいつか
- NOAA の SOI 図と大きく違わないか
12. 解答ページ
完全スクリプトは別ページにしてある。まず自分で考えてから必要なときだけ参照すること。
▶ 解答ページへ13. 提出方法(重要)
本課題は、Jupyter Lab で作成した Notebook を HTML として保存し、Teams に提出すること。
提出手順
- Jupyter Lab 上で Notebook を開く
- 上部メニューから File → Save and Export Notebook As → HTML を選択する
- HTML ファイルを保存する
- 保存した HTML ファイルを Teams に提出する
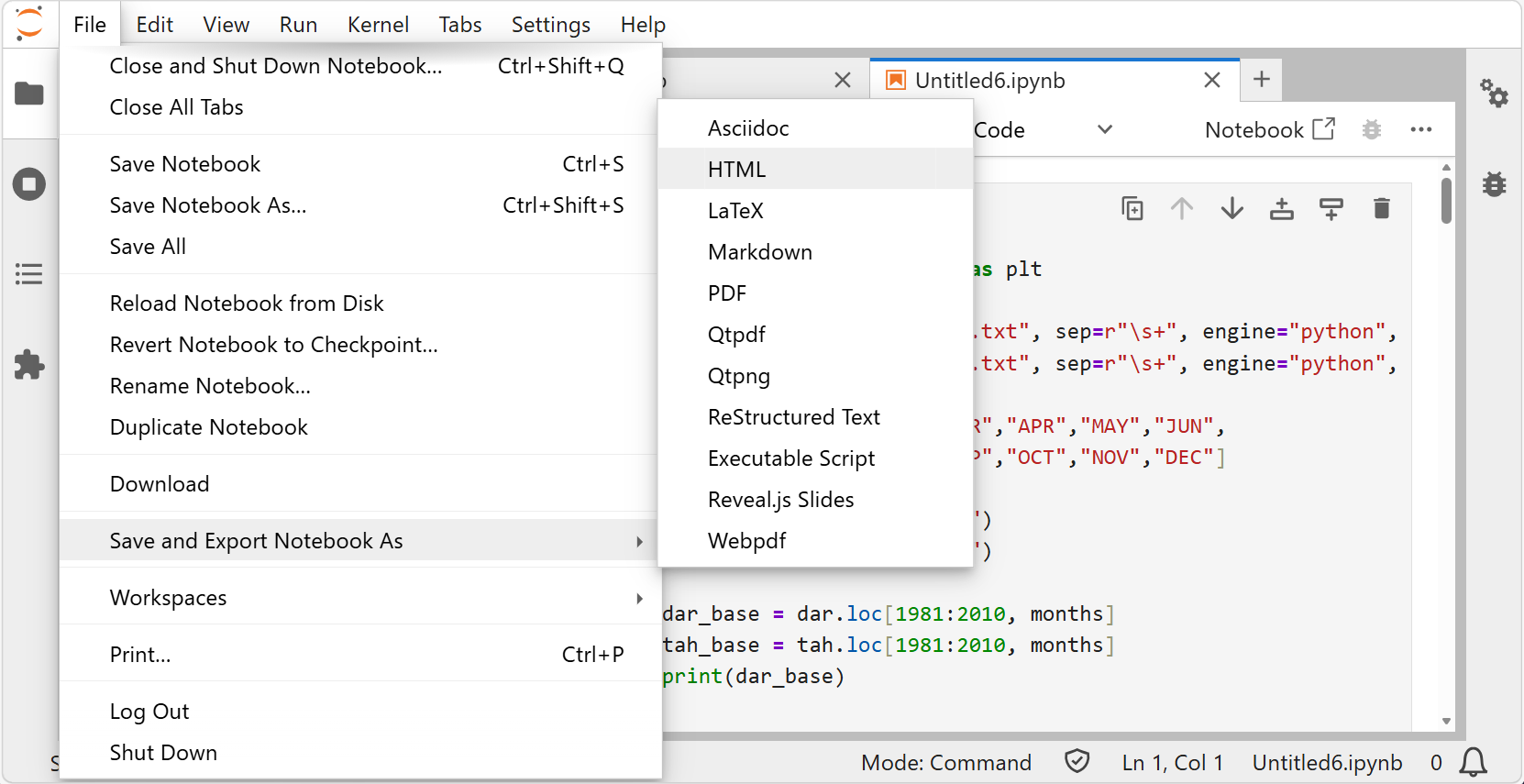
Jupyter Lab のメニューから HTML として保存する。
.ipynb のままでは提出しないこと。 必ず HTML に変換して提出すること。